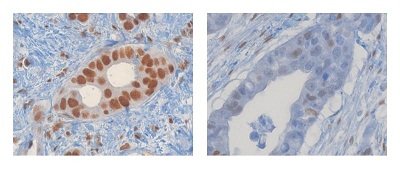
Google liefert gute Suchergebnisse, weil es nicht nur Webseiten, sondern auch die Hyperlinks zwischen ihnen berücksichtigt. Eine ähnlichen Strategie haben Forscher nun in der Krebsforschung genutzt. Sie setzten eine modifizierte Version von Googles PageRank-Algorithmus ein, um 20.000 Proteine nach ihrem Einfluss auf das Voranschreiten des Bauschspeicheldrüsenkrebses zu untersuchen. Wie die Wissenschaftler im Fachjournal „PLoS Computational Biology“ berichten, fanden sie dabei sieben Proteine, die dabei helfen können, die Aggressivität eines diagnostizierten Tumors anhand des Tumorgewebes zu bestimmen. Anhand dieser Information kann dann ein behandelnder Arzt entscheiden, ob dem Patienten eine Chemotherapie nutzt oder nicht.
Gesucht haben die Forscher der TU Dresden in ihrer Studie nach sogenannten Biomarkern – Molekülen, die vom Tumor produziert werden und die den weiteren Verlauf oder das Wiederauftreten einer Krebserkrankung anzeigen können. Trotz intensiver weltweiter Forschung wurden bisher nur wenige verlässliche Biomarker gefunden. Ein wesentliches Problem ist die große Anzahl an möglichen Molekülen und die Tatsache, dass in Studien gefundene Marker in anderen Studien oft nicht reproduzierbar sind.
In der aktuellen Studie lösten die Forscher dieses Problem durch eine der Suchmaschine Google abgeschauten Strategie: Proteine in einer Zelle gehen häufig Partnerschaften ein, um gemeinsam eine Aufgabe zu erfüllen. Dieses soziale Netzwerk der Proteine, das „Protein-Facebook“ sozusagen, half entscheidend bei der Biomarkersuche. „Nachdem wir die Netzwerkinformation der Proteine in unsere Analyse aufgenommen hatten, haben sich unsere Ergebnisse deutlich verbessert und konnten reproduziert werden“, erläutet Christof Winter vom BIOTEC der TU Dresden. Wissenschaftler der University of North Carolina hatten bereits zuvor sechs Proteine gefunden, welche die Aggressivität von Bauchspeicheldrüsenkrebs anzeigen. Eines dieser Proteine wurde auch in der Dresdner Studiegefunden.
Weg bis zur Anwendung ist noch weit
Obwohl die neuen Biomarker eine Verbesserung gegenüber aktuell verwendeten Methoden darstellen, ist es noch ein weiter Weg bis zur klinischen Anwendung. In einer größeren Studie muss erst gezeigt werden, wie gut die Marker wirklich die Proteine herausfiltern, die den weiteren Verlauf der Krebserkrankung anzeigen. „Es wäre ein sehr wichtiger Schritt, aggressive Therapien wie eine Chemotherapie nur bei den Patienten einzusetzen, die mit großer Wahrscheinlichkeit davon profitieren werden. Dabei könnten solche prädiktiven Tests helfen“, sagt Robert Grützmann, Oberarzt und Wissenschaftler in der Klinik für Viszeral-, Thorax- und Gefäßchirurgie des UKD.
Derzeit erkranken nach Angaben der Deutschen Krebshilfe in Deutschland jedes Jahr 14.200 Menschen neu an Bauspeicheldrüsenkrebs. Mehr noch als bei manch anderer Krebsart gilt bei Bauchspeicheldrüsenkrebs, dass die Heilungs- und Überlebenschancen umso besser sind, je früher der Tumor erkannt und behandelt wird. Somit ist es auch eine wichtige Frage, ob und wie die Marker dabei helfen können, Medikamente zu entwickeln, die das Krebswachstum hemmen. In Zusammenarbeit mit der Dresdner Firma „RESprotect“, welche sich auf die Medikamentenentwicklung bei Bauchspeicheldrüsenkrebs spezialisiert hat, werden die Wissenschaftler nun daran arbeiten, ihre Erkenntnisse langfristig in eine verbesserte Therapie zu übertragen. (PLoS Computational Biology, 2012; doi: 10.1371/journal.pcbi.1002511)
(Technische Universität Dresden, 21.05.2012 – NPO)