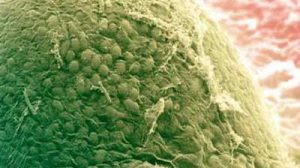
Fische können darin kaum überleben, Menschen bekämen Hautverätzungen: einige Tagebauseen in der Lausitz und der Oberpfalz sind so sauer wie reiner Essig. Jetzt haben Forscher in diesen Seen die säuretolerante Mikrobenwelt untersucht und dabei eine bisher völlig unbekannte Art entdeckt. Identifziert wurde sie durch ihre ribosomale RNA. Die extrem toleranten Mikroben könnten möglicherweise in der Biotechnologie oder zur biologischen Abwasserreinigung genutzt werden.
Das „Restloch“ RL107 in der Lausitz und der Lindensee in der Oberpfalz sind Überreste des Braunkohletagebaus, ehemalige Lagerstätten, die im Laufe der Zeit überschwemmt oder geflutet wurden und in denen Pyrit – ein bei der Lagerung von Braunkohle entstehendes Mineral – von Mikroorganismen zersetzt wird. Bei diesem Prozess entsteht Schwefelsäure, die die Gewässer so sauer wie Essig macht. Volker Huß von der Universität Erlangen-Nürnberg (FAU) hat nun die Lebenswelt dieser Seen im Rahmen eines Forschungsprojekts der Deutschen Forschungsgemeinschaft (DFG) genauer untersucht.
In einem Verfahren, das als „environmental PCR“ bezeichnet wird, extrahierte der Wissenschaftler die in Wasserproben vorhandenen unterschiedlichen RNA-Sequenzen und verglich sie anschließend mit einer Datenbank, in der tausende weitere solche Sequenzen gespeichert sind. Die ribosomale RNA eignet sich besonders gut zur Identifizierung verschiedener Organismen, da sie sich im Laufe der Evolution nur geringfügig verändert hat. Je ähnlicher die RNA-Sequenzen sind, desto später haben sich die Organismen in der Evolution voneinander abgespalten.
Artzuordnung mit Hilfe der RNA
„Über die Sequenzen lässt sich ermitteln, wann sich die Entwicklungslinien getrennt haben. Vergleicht man sie dann miteinander, entsteht eine Art Familienstammbaum, der uns zeigt, was für eine ungeheure Vielfalt dieser Mikroorganismen existiert“, sagt Huß. „Mit anderen Untersuchungsmethoden, wie zum Beispiel mit einem Mikroskop, wäre eine exakte Bestimmung wesentlich schwieriger oder gar unmöglich.“
Ingesamt 23 verschiedene Mikroorganismen isolierte Huß aus dem Lindensee. Im „Restloch“, das einen noch höheren Säuregehalt aufweist, konnte er nur noch neun verschiedene Organismen identifizieren. „Dabei hat sich gezeigt, dass die uns bekannten und charakterisierten Organismen nur einen Bruchteil der natürlich vorkommenden Biodiversität ausmachen“, erläutert Huß das Forschungsergebnis. Eine der gefundenen Sequenzen konnte sogar keiner der bislang bekannten Evolutionslinien der Organismen zugeordnet werden.
Auch Grünalge bildet Cyste
Auch bereits bekannte Organismen unterzog Huß einer eingehenden Untersuchung. Bei der elektronenmikroskopischen Analyse einer aus den Seen isolierten Grünalge machte er eine weitere Entdeckung: Manche Gruppen von Algen besitzen einen Schutzmechanismus. Ähnlich wie Igel rollen sie sich bei äußeren Einflüssen, die sie schädigen könnten, zusammen zu Kugeln, so genannten Cysten. Auf diese Weise können sie jahrelang auch unter widrigsten Bedingungen überleben. Ein derartiger Mechanismus war jedoch innerhalb der Gruppe von Grünalgen, zu denen die von Huß erfasste Alge gehört, bisher nicht bekannt. Diese Alge bildet aber cystenähnliche Strukturen aus, die möglicherweise als Vorstufen der Evolution zu einer echten Cystenbildung angesehen werden können.
Langfristig gesehen könnte die Untersuchung der säuretoleranten Mikroorganismen in der Biotechnologie genutzt werden. Denkbar wäre ein Einsatz zum Beispiel in der biologischen Abwasserreinigung.
(Universität Erlangen-Nürnberg, 11.10.2010 – NPO)